Paleopolyploidie - Paleopolyploidy

Paleopolyploidie je výsledkem duplikace genomu ke kterému došlo nejméně před několika miliony let (MYA). Taková událost by mohla buď zdvojnásobit genom jednoho druhu (autopolyploidie ) nebo kombinovat dva druhy (alopolyploidie ). Kvůli funkčnosti nadbytek, geny jsou rychle umlčeny nebo ztraceny z duplikovaných genomů. Většina paleopolyploidů během evolučního času ztratila své polyploidní stav prostřednictvím procesu zvaného diploidizacea jsou v současné době zvažovány diploidy např. pekařské droždí,[1] Arabidopsis thaliana,[2] a možná lidé.[3][4][5][6]
Paleopolyploidie je rozsáhle studována v liniích rostlin. Bylo zjištěno, že téměř všechny kvetoucí rostliny prošly během své evoluční historie alespoň jednou kolo duplikace genomu. Zdvojení starověkého genomu se také vyskytuje u raného předka obratlovců (včetně lidské linie) poblíž původu kostnaté ryby a další v kmenové linii teleost ryb.[7] Důkazy naznačují, že pekařské droždí (Saccharomyces cerevisiae ), který má kompaktní genom, zažil během své evoluční historie polyploidizaci.
Termín mezopolyploid je někdy používán pro druhy, které prošly událostmi množení celého genomu (duplikace celého genomu, triplifikace celého genomu atd.) v novější historii, například za posledních 17 milionů let.[8]
Eukaryoty
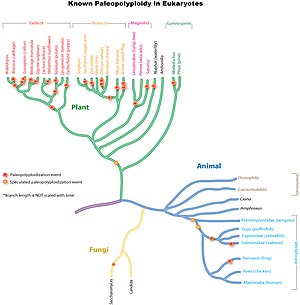
Zdvojování starověkého genomu je velmi rozšířené eukaryotický linie, zejména v rostlinách. Studie naznačují, že společný předchůdce Poaceae Rodina trávy, která zahrnuje důležité druhy plodin, jako je kukuřice, rýže, pšenice a cukrová třtina, sdílela duplikaci celého genomu o 70 před miliony let.[9] Ve více starodávných monokotových liniích došlo k jednomu nebo pravděpodobně několika kolům dalších duplikací celého genomu, které však nebyly sdíleny s rodovými eudicots.[10] K dalším nezávislým novějším duplikacím celého genomu došlo v liniích vedoucích ke kukuřici, cukrové třtině a pšenici, ale nikoli k rýži, čiroku nebo proso.
Polyploidní událost 160 před miliony let se předpokládá, že vytvořil rodovou linii, která vedla ke všem moderním kvetoucím rostlinám.[11] Tato událost paleopolyploidie byla studována sekvenováním genomu staré kvetoucí rostliny, Amborella trichopoda.[12]
Základní eudikoti sdíleli také společnou triplikaci celého genomu (paleohexaploidii), která se podle odhadů vyskytla po jednoděložná rostlina -eudicot divergence, ale před divergencí rosidy a asteroidy.[13][14][15] Mnoho druhů eudicot zažilo další duplikace nebo triplikace celého genomu. Například modelový závod Arabidopsis thaliana, první rostlina, která má celý svůj genom sekvenován, zažila nejméně dvě další kola duplikace celého genomu od duplikace sdílené základními eudikoty.[2] Poslední událost se odehrála před divergencí Arabidopsis a Brassica počty řádků, o 20 před miliony let na 45 před miliony let. Mezi další příklady patří sekvenované eudikotické genomy jablek, sóji, rajčat, bavlny atd.
Ve srovnání s rostlinami je paleopolyploidie v živočišné říši mnohem vzácnější. Byl identifikován hlavně u obojživelníků a kostnatých ryb. Ačkoli některé studie naznačovaly, že jednu nebo více běžných duplikací genomu sdílejí všichni obratlovci (včetně lidí), důkazy nejsou tak silné jako v ostatních případech, protože duplikace, pokud existují, se staly tak dávno a záležitost je stále pod rozprava. Myšlenka, že obratlovci sdílejí společnou duplikaci celého genomu, je známá jako 2R hypotéza. Mnoho vědců se zajímá o důvod, proč živočišné linie, zejména savci, mají tolik méně duplikací celého genomu než linie rostlin.
Dobře podporovaná paleopolyploidie byla nalezena v pekařských kvasnicích (Saccharomyces cerevisiae), navzdory svému malému kompaktnímu genomu (~ 13 Mb / s), po odchylce od běžných kvasinek Kluyveromyces waltii.[16] Zefektivněním genomu kvasinky během evolučního času ztratily 90% duplikovaného genomu a jsou nyní uznávány jako diploidní organismus.
Metoda detekce
Duplikované geny lze identifikovat prostřednictvím sekvenční homologie na úrovni DNA nebo bílkovin. Paleopolyploidii lze identifikovat jako masivní genovou duplikaci najednou pomocí a molekulární hodiny. Rozlišovat mezi duplikací celého genomu a sbírkou (běžnějších) singlů genová duplikace události, často se používají následující pravidla:

- Duplikované geny jsou umístěny ve velkých duplikovaných blocích. Duplikace jednoho genu je náhodný proces a má tendenci vytvářet duplikované geny rozptýlené po celém genomu.
- Duplikované bloky se nepřekrývají, protože byly vytvořeny současně. Segmentová duplikace v genomu může splnit první pravidlo; ale několik nezávislých segmentových duplikací se mohlo navzájem překrývat.
Teoreticky by dva duplikované geny měly mít stejný „věk“; to znamená, že divergence sekvence by měla být stejná mezi dvěma geny duplikovanými paleopolyploidií (homeologové ). Synonymní substituce hodnotit, Ks, se často používá jako molekulární hodiny k určení času genové duplikace. Paleopolyploidie je tedy identifikována jako „vrchol“ v grafu duplikátu počtu vs. Ks (zobrazeno vpravo).
Duplikační události, které se v historii různých evolučních linií vyskytly už dávno, je obtížné odhalit kvůli následné diploidizaci (tak, že se polyploid začne chovat cytogeneticky jako diploid v průběhu času), protože mutace a genové překlady postupně vytvářejí jednu kopii každé chromozom na rozdíl od svého protějšku. To obvykle vede k nízké důvěře v identifikaci velmi staré paleopolyploidie.
Evoluční význam
Paleopolyploidizační události vedou k masivním buněčným změnám, včetně zdvojnásobení genetického materiálu, změn genové exprese a zvětšení velikosti buněk. Ztráta genů během diploidizace není zcela náhodná, ale silně vybírána. Geny z velkých genových rodin jsou duplikovány. Na druhou stranu jednotlivé geny nejsou duplikovány.[je zapotřebí objasnění ] Celkově může mít paleopolyploidie krátkodobý i dlouhodobý evoluční účinek na kondici organismu v přirozeném prostředí.
- Vylepšená fenotypová evoluce
- Duplikace celého genomu může zvýšit rychlost a účinnost, jakou organismy získávají nové biologické vlastnosti. Jeden test této hypotézy, který porovnával vývojové rychlosti v inovaci u raných teleostních ryb (s duplicitními genomy), u raných holostejských ryb (bez duplikovaných genomů), však mezi nimi nenalezl malý rozdíl.[7]
- Rozmanitost genomu
- Zdvojnásobení genomu poskytlo organismu redundantní alely, které se mohou volně vyvíjet s malým selekčním tlakem. Duplikované geny mohou podstoupit neofunkcionalizace nebo subfunkcionalizace které by mohly pomoci organismu přizpůsobit se novému prostředí nebo přežít různé stresové podmínky.
- Hybridní ráznost
- Polyploidy mají často větší buňky a ještě větší orgány. Mnoho důležitých plodin, včetně pšenice, kukuřice a bavlna, jsou paleopolyploidy, které byly vybrány pro domestikaci starými národy.
- Speciace
- Bylo navrženo, že mnoho polyploidizačních událostí vytvořilo nové druhy, a to díky získání adaptivních rysů nebo sexuální nekompatibilitou s jejich diploidními protějšky. Příkladem může být nedávný speciace alopolyploidu Spartina — S. anglica; polyploidní rostlina je tak úspěšná, že je uvedena jako invazivní druhy v mnoha regionech.
Alopolyploidie a autopolyploidie
Existují dvě hlavní divize polyploidie, alopolyplody a autopolyploidy. Alopolyploidy vznikají v důsledku hybridizace dvou příbuzných druhů, zatímco autopolyploidy vznikají z duplikace genomu druhu v důsledku hybridizace dvou stejných rodičů,[17] nebo somatické zdvojnásobení v reprodukční tkáni rodiče. Předpokládá se, že alopolyploidní druhy jsou v přírodě mnohem častější,[17] pravděpodobně proto, že alopolyploidy dědí různé genomy, což vede ke zvýšení heterozygotnost, a tedy vyšší kondici. Tyto různé genomy vedou ke zvýšené pravděpodobnosti velkých genomových reorganizací,[17][18] což může být škodlivé nebo výhodné. Autopolyploidie je však obecně považována za neutrální proces,[19] i když se předpokládá, že autopolyploidie může sloužit jako užitečný mechanismus k vyvolání speciace, a tudíž napomáhání schopnosti organismu rychle kolonizovat na nových stanovištích, aniž by prošla časově náročným a nákladným obdobím genomové reorganizace, které zažívají alopolyploidní druhy. Jeden běžný zdroj autopolyploidie v rostlinách pochází z „dokonalých květů“, které jsou schopné samoopylení nebo „samoopelení“. To spolu s chybami v redukční dělení buněk které vedou k aneuploidie, může vytvořit prostředí, kde je autopolyploidie velmi pravděpodobná. Tuto skutečnost lze využít v laboratorním prostředí pomocí kolchicin inhibovat chromozóm segregace během meiózy, vytváření syntetických autopolyploidních rostlin.
Po událostech polyploidie existuje několik možných osudů pro duplikování geny; obě kopie mohou být zachovány jako funkční geny, ke změně genové funkce může dojít v jedné nebo obou kopiích, umlčování genů může maskovat jednu nebo obě kopie nebo může dojít k úplné ztrátě genu.[17][20] Polyploidní události budou mít za následek vyšší úrovně heterozygotnosti a v průběhu času mohou vést ke zvýšení celkového počtu funkčních genů v genomu. Jak čas plyne po události duplikace genomu, mnoho genů změní funkci v důsledku změny ve funkci duplikátu genu jak pro alo-, tak pro autopolyploidní druhy, nebo dojde ke změnám v genové expresi způsobené genomickými přesmyky vyvolanými duplikací genomu v alopolyploidech . Pokud jsou zachovány obě kopie genu a tím se zdvojnásobí počet kopií, existuje šance, že dojde k proporcionálnímu zvýšení exprese tohoto genu, což povede k dvojnásobnému zvýšení mRNA vytvářený přepis. Existuje také možnost, že transkripce duplikovaného genu bude down-regulovaná, což povede k méně než dvojnásobnému zvýšení transkripce tohoto genu, nebo že duplikační událost přinese více než dvojnásobné zvýšení transkripce.[21] U jednoho druhu Glycinová dolichocarpa (blízký příbuzný sója, Glycin max), bylo pozorováno, že po duplikaci genomu zhruba před 500 000 lety došlo k 1,4násobnému zvýšení transkripce, což naznačuje, že došlo k proporcionálnímu poklesu transkripce vzhledem k počtu kopií genů po události duplikace.[21]
Obratlovci jako paleopolyploid
Hypotéza paleopolyploidie obratlovců vznikla již v 70. letech 20. století a byla navržena biologem Susumu Ohno. Tvrdil, že genom obratlovců nemůže dosáhnout své složitosti bez rozsáhlých duplikací celého genomu. Hypotéza „dvě kola duplikace genomu“ (2R hypotéza ) vznikl a získal si popularitu, zejména u vývojových biologů.
Někteří vědci zpochybnili hypotézu 2R, protože předpovídá, že genomy obratlovců by měly mít poměr genů 4: 1 ve srovnání s genomy bezobratlých, což však nepodporují nálezy ze 48 projektů genomu obratlovců dostupných v polovině roku 2011. Například lidský genom se skládá z ~ 21 000 genů kódujících bílkoviny podle údajů z června 2011 v centrech pro analýzu genomu UCSC a Ensembl[Citace je zapotřebí ] zatímco průměrná velikost genomu bezobratlých je asi 15 000 genů. The amphioxus sekvence genomu poskytla podporu pro hypotézu dvou kol duplikace celého genomu, následovanou ztrátou duplikovaných kopií většiny genů.[22] Další argumenty proti 2R byly založeny na chybějící topologii stromu (AB) (CD) mezi čtyřmi členy genové rodiny obratlovců. Pokud by se však obě duplikace genomu vyskytly těsně vedle sebe, neočekávali bychom, že najdeme tuto topologii.[23] Nedávná studie vygenerovala mořský mihule genetická mapa, která poskytla silnou podporu hypotéze, že k jedné duplikaci celého genomu došlo v linii bazálních obratlovců, předcházelo a následovalo několik evolučně nezávislých segmentových duplikací, které se vyskytly během vývoje strunatců.[24]
Viz také
Reference
- ^ Kellis M, Birren BW, Lander ES (duben 2004). "Důkaz a evoluční analýza duplikace starověkého genomu v kvasinkách Saccharomyces cerevisiae". Příroda. 428 (6983): 617–24. Bibcode:2004 Natur.428..617K. doi:10.1038 / nature02424. PMID 15004568. S2CID 4422074.
- ^ A b Bowers JE, Chapman BA, Rong J, Paterson AH (březen 2003). "Odhalení evoluce genomu krytosemenných rostlin fylogenetickou analýzou událostí chromozomální duplikace". Příroda. 422 (6930): 433–8. Bibcode:2003 Natur.422..433B. doi:10.1038 / nature01521. PMID 12660784. S2CID 4423658.
- ^ Smith JJ, Kuraku S, Holt C, Sauka-Spengler T, Jiang N, Campbell MS a kol. (Duben 2013). „Sekvenování genomu mihule mořské (Petromyzon marinus) poskytuje poznatky o vývoji obratlovců“. Genetika přírody. 45 (4): 415–21, 421e1-2. doi:10.1038 / ng.2568. PMC 3709584. PMID 23435085.
- ^ Wolfe KH (Květen 2001). „Včerejší polyploidy a tajemství diploidizace“. Recenze přírody. Genetika. 2 (5): 333–41. doi:10.1038/35072009. PMID 11331899. S2CID 20796914.
- ^ Blanc G, Wolfe KH (Červenec 2004). „Rozšířená paleopolyploidie u modelových druhů rostlin odvozená z věkových distribucí duplicitních genů“. Rostlinná buňka. 16 (7): 1667–78. doi:10.1105 / tpc.021345. PMC 514152. PMID 15208399.
- ^ Blanc G, Wolfe KH (Červenec 2004). „Funkční divergence duplikovaných genů vytvořených polyploidií během vývoje Arabidopsis“. Rostlinná buňka. 16 (7): 1679–91. doi:10.1105 / tpc.021410. PMC 514153. PMID 15208398.
- ^ A b Clarke JT, Lloyd GT, Friedman M (říjen 2016). „Málo důkazů o zvýšené fenotypové evoluci v časných teleostech ve srovnání s jejich sesterskou skupinou žijících fosilií“. Sborník Národní akademie věd Spojených států amerických. 113 (41): 11531–11536. doi:10.1073 / pnas.1607237113. PMC 5068283. PMID 27671652.
- ^ Wang X „Wang H, Wang J, Sun R, Wu J, Liu S a kol. (Srpen 2011). „Genom mezopolyploidního druhu plodiny Brassica rapa“. Genetika přírody. 43 (10): 1035–9. doi:10,1038 / ng. 919. PMID 21873998. S2CID 205358099.
- ^ Paterson AH, Bowers JE, Chapman BA (červen 2004). „Starověká polyploidizace předcházející divergenci obilovin a její důsledky pro srovnávací genomiku“. Sborník Národní akademie věd Spojených států amerických. 101 (26): 9903–8. Bibcode:2004PNAS..101.9903P. doi:10.1073 / pnas.0307901101. PMC 470771. PMID 15161969.
- ^ Tang H, Bowers JE, Wang X, Paterson AH (leden 2010). „Porovnání genomu krytosemenných rostlin odhaluje časnou polyploidii v linii jednoděložných rostlin“. Sborník Národní akademie věd Spojených států amerických. 107 (1): 472–7. Bibcode:2010PNAS..107..472T. doi:10.1073 / pnas.0908007107. PMC 2806719. PMID 19966307.
- ^ Callaway E (prosinec 2013). „Keřový genom odhaluje tajemství květinové síly“. Příroda. doi:10.1038 / příroda.2013.14426. S2CID 88293665.
- ^ Adams K (prosinec 2013). „Genomika. Genomické stopy po rodové kvetoucí rostlině“. Věda. 342 (6165): 1456–7. Bibcode:2013Sci ... 342.1456A. doi:10.1126 / science.1248709. PMID 24357306. S2CID 206553839.
- ^ Tang H, Wang X, Bowers JE, Ming R, Alam M, Paterson AH (prosinec 2008). „Rozluštění starověké hexaploidie prostřednictvím vícenásobně zarovnaných genových map krytosemenných rostlin“. Výzkum genomu. 18 (12): 1944–54. doi:10.1101 / gr.080978.108. PMC 2593578. PMID 18832442.
- ^ Jaillon O, Aury JM, Noel B, Policriti A, Clepet C, Casagrande A a kol. (Září 2007). „Sekvence genomu vinné révy naznačuje rodovou hexaploidizaci u hlavních krytosemenných rostlin“. Příroda. 449 (7161): 463–7. Bibcode:2007Natur.449..463J. doi:10.1038 / nature06148. PMID 17721507.
- ^ Tang H, Bowers JE, Wang X, Ming R, Alam M, Paterson AH (duben 2008). "Syntenita a kolinearita v rostlinných genomech". Věda. 320 (5875): 486–8. Bibcode:2008Sci ... 320..486T. doi:10.1126 / science.1153917. PMID 18436778. S2CID 206510918.
- ^ Wong S, Butler G, Wolfe KH (Červenec 2002). "Vývoj genového řádu a paleopolyploidie v kvasinkách hemiascomycete". Sborník Národní akademie věd Spojených států amerických. 99 (14): 9272–7. Bibcode:2002PNAS ... 99,9272W. doi:10.1073 / pnas.142101099. PMC 123130. PMID 12093907.
- ^ A b C d Soltis PS, Soltis DE (červen 2000). „Role genetických a genomických atributů pro úspěch polyploidů“. Sborník Národní akademie věd Spojených států amerických. 97 (13): 7051–7. Bibcode:2000PNAS ... 97.7051S. doi:10.1073 / pnas.97.13.7051. PMC 34383. PMID 10860970.
- ^ Parisod C, Holderegger R, Brochmann C (duben 2010). „Evoluční důsledky autopolyploidie“. Nový fytolog. 186 (1): 5–17. doi:10.1111 / j.1469-8137.2009.03142.x. PMID 20070540.
- ^ Parisod C, Holderegger R, Brochmann C (duben 2010). „Evoluční důsledky autopolyploidie“. Nový fytolog. 186 (1): 5–17. doi:10.1111 / j.1469-8137.2009.03142.x. PMID 20070540.
- ^ Wendel JF (2000). Evoluce genomu v polyploidech. Molekulární biologie rostlin. 42. str. 225–249. doi:10.1007/978-94-011-4221-2_12. ISBN 978-94-010-5833-9. PMID 10688139.
- ^ A b Coate JE, Doyle JJ (2010). „Kvantifikace celé velikosti transkriptomu, předpoklad pro pochopení evoluce transkriptomu napříč druhy: příklad z rostlinného alopolyploidu“. Biologie genomu a evoluce. 2: 534–46. doi:10.1093 / gbe / evq038. PMC 2997557. PMID 20671102.
- ^ Putnam NH, Butts T, Ferrier DE, Furlong RF, Hellsten U, Kawashima T a kol. (Červen 2008). „Amphioxus genom a vývoj karyotypu strunatců“. Příroda. 453 (7198): 1064–71. Bibcode:2008 Natur.453.1064P. doi:10.1038 / nature06967. PMID 18563158.
- ^ Furlong RF, Holland PW (duben 2002). „Byli obratlovci oktoploidní?“. Filozofické transakce Královské společnosti v Londýně. Série B, Biologické vědy. 357 (1420): 531–44. doi:10.1098 / rstb.2001.1035. PMC 1692965. PMID 12028790.
- ^ Smith JJ, Keinath MC (srpen 2015). „Meiotická mapa mořské mihule zlepšuje rozlišení duplikací genomu starověkých obratlovců“. Výzkum genomu. 25 (8): 1081–90. doi:10,1101 / gr.184135.114. PMC 4509993. PMID 26048246.
Další čtení
- Adams KL, Wendel JF (duben 2005). "Polyploidie a vývoj genomu v rostlinách". Aktuální názor na biologii rostlin. 8 (2): 135–41. doi:10.1016 / j.pbi.2005.01.001. PMID 15752992.
- Cui L, Wall PK, Leebens-Mack JH, Lindsay BG, Soltis DE, Doyle JJ a kol. (Červen 2006). „Rozsáhlé duplikace genomu v celé historii kvetoucích rostlin“. Výzkum genomu. 16 (6): 738–49. doi:10,1101 / gr. 4825606. PMC 1479859. PMID 16702410.
- Comai L (listopad 2005). "Výhody a nevýhody bytí polyploidní". Recenze přírody. Genetika. 6 (11): 836–46. doi:10.1038 / nrg1711. PMID 16304599. S2CID 3329282.
- Otto SP, Whitton J (2000). "Výskyt a vývoj polyploidů". Výroční přehled genetiky. 34 (1): 401–437. CiteSeerX 10.1.1.323.1059. doi:10.1146 / annurev.genet.34.1.401. PMID 11092833.
- Makalowski W (květen 2001). „Jsme polyploidy? Stručná historie jedné hypotézy“. Výzkum genomu. 11 (5): 667–70. doi:10,1101 / gr.188801. PMID 11337465.
- Kellis M, Birren BW, Lander ES (duben 2004). "Důkaz a evoluční analýza duplikace starověkého genomu v kvasinkách Saccharomyces cerevisiae". Příroda. 428 (6983): 617–24. Bibcode:2004 Natur.428..617K. doi:10.1038 / nature02424. PMID 15004568. S2CID 4422074.
